Resultados Preliminares
Análise dos 144 genomas clínicos de K. pneumoniae
Os resultados a seguir derivam exclusivamente dos 144 genomas clínicos já sequenciados e depositados (BioProject PRJNA1185159; SRA SRP545647).
Genomas sequenciados por hospital e fase
O estudo multicêntrico gerou 368 genomas (224 K. pneumoniae + 144 A. baumannii), distribuídos por hospital e fase de intervenção:
| Hospital | Espécie | Pré-Intervenção | Intervenção | Pós-Intervenção | Total |
|---|---|---|---|---|---|
| HSP | K. pneumoniae | 6 | 23 | 0 | 29 |
| A. baumannii | 3 | 5 | 0 | 8 | |
| HGPE | K. pneumoniae | 5 | 9 | 0 | 14 |
| A. baumannii | 6 | 36 | 0 | 42 | |
| HED | K. pneumoniae | 0 | 42 | 0 | 42 |
| A. baumannii | 9 | 38 | 0 | 47 | |
| HGPI | K. pneumoniae | 7 | 42 | 35 | 84 |
| A. baumannii | 0 | 4 | 0 | 4 | |
| HGG | K. pneumoniae | 0 | 13 | 0 | 13 |
| A. baumannii | — | — | — | 0 | |
| HMB | K. pneumoniae | 6 | 36 | 0 | 42 |
| A. baumannii | 3 | 40 | 0 | 43 | |
| Total | K. pneumoniae | 24 | 165 | 35 | 224 |
| A. baumannii | 21 | 123 | 0 | 144 | |
| Total geral | 45 | 288 | 35 | 368 |
Dos 224 genomas de K. pneumoniae, 144 não suscetíveis a carbapenêmicos (CIM de meropenem ≥ 2 µg/mL) compõem o conjunto principal de análise.
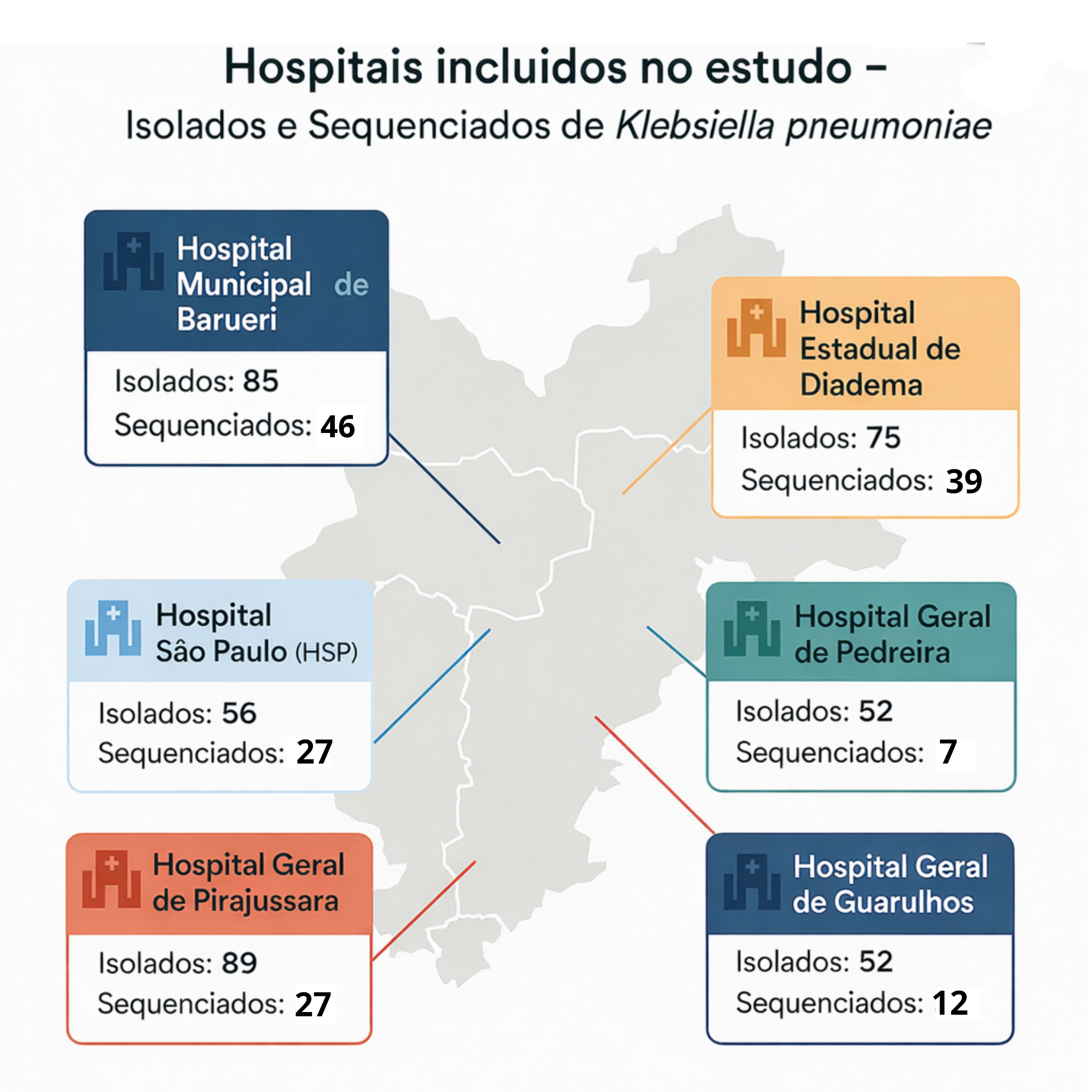
Distribuição dos 144 genomas de K. pneumoniae por hospital
| Sigla | Hospital | n (%) |
|---|---|---|
| HMB | Hospital Municipal de Barueri | 44 (30,6%) |
| HED | Hospital Estadual de Diadema | 37 (25,7%) |
| HGPI | Hospital Geral de Pirajussara | 24 (16,7%) |
| HSP | Hospital São Paulo | 23 (16,0%) |
| HGG | Hospital Geral de Guarulhos | 10 (6,9%) |
| HGPE | Hospital Geral de Pedreira | 6 (4,2%) |
| Total | 144 (100%) |
Distribuição de Sequence Types (ST)
Três clones de alto risco globalmente disseminados predominam na coleção:
| ST | HED | HGG | HGPE | HGPI | HMB | HSP | Total (%) |
|---|---|---|---|---|---|---|---|
| ST11 | 16 | 2 | 2 | 19 | 12 | 8 | 59 (41,0%) |
| ST16 | 15 | 7 | 2 | 5 | 12 | 10 | 51 (35,4%) |
| ST258 | 4 | 0 | 1 | 0 | 16 | 5 | 26 (18,1%) |
| Outros | 2 | 1 | 1 | 0 | 4 | 0 | 8 (5,5%) |
| Total | 37 | 10 | 6 | 24 | 44 | 23 | 144 |
ST11 (41,0%), ST16 (35,4%) e ST258 (18,1%) juntos representam 94,4% de toda a coleção. STs minoritários incluem ST147, ST101, ST268, ST273, ST3520 e ST17.
Perfil de resistência e resistoma
Carbapenemases
| Perfil | n | % |
|---|---|---|
| KPC-2 positivo | 139 | 96,5% |
| NDM-1 positivo | 4 | 2,8% |
| KPC-2 + NDM-1 (co-produção) | 1 | 0,7% |
Quatro isolados portam NDM-1, incluindo um caso de co-produção KPC-2 + NDM-1 (ST17, HGPE). Dois isolados NDM-positivos são também resistentes a colistina.
Principais genes de resistência
| Gene / Classe | Função | n | % |
|---|---|---|---|
| blaKPC-2 | Carbapenemase | 130 | 90,3% |
| blaCTX-M-15 | ESBL | 91 | 63,2% |
| blaCTX-M-2 | ESBL | 52 | 36,1% |
| oqxAB | Sistema de efluxo | 142 | 98,6% |
| aac(6’)-Ib | Resistência a aminoglicosídeos | 125 | 86,8% |
| qnrB | Resistência a fluoroquinolonas | 82 | 56,9% |
| qacEΔ1 | Tolerância a QAC/desinfetantes | 119 | 82,6% |
| smr | Bomba de efluxo (QAC) | 62 | 43,1% |
Beta-lactamases por ST
| Enzima | n | % | STs principais |
|---|---|---|---|
| KPC-2 | 139 | 96,5% | Todos |
| NDM-1 | 4 | 2,8% | ST3520, ST17, ST11, ST147 |
| CTX-M-15 | 53 | 36,8% | ST16 (principal), ST11 |
| CTX-M-14 | 27 | 18,8% | ST258 (exclusivo) |
| CTX-M-2 | 24 | 16,7% | ST11 (principal) |
Mutações em porinas
| Porina | n | % |
|---|---|---|
| OmpK35 | 130 | 90,3% |
| OmpK36 | 112 | 77,8% |
| Ambas (OmpK35 + OmpK36) | 108 | 75,0% |
Fatores de virulência
| Fator | n | % | STs com >50% |
|---|---|---|---|
| Yersiniabactina (ybt) | 113 | 78,5% | ST11 (100%), ST258 (88,5%), ST16 (51%) |
| Colibactina (clb) | 60 | 41,7% | ST11 (84,7%), ST258 (34,6%) |
A presença de colibactina está fortemente associada ao ST11 (84,7%), enquanto está ausente no ST16. ST11 combina perfil de alta virulência com multirresistência extensa.
Perfis genotípicos por Sequence Type
ST11 (n=59, 41,0%)
- Carbapenemase: KPC-2 (98,3%), NDM-1 (1,7%)
- ESBL: CTX-M-2 (39,0%), CTX-M-15 (13,6%)
- rmtB (resistência a aminoglicosídeos): 40,7%
- Mutações QRDR: 100% — GyrA-Ser83Ile + ParC-Ser80Ile
- Porinas: OmpK35 (84,7%), OmpK36 (84,7%)
- Virulência: ybt+ (100%), clb+ (84,7%)
- Sorotipo: KL64 / O2α.1
Conclusão: clone de alta virulência combinado com multirresistência extensa.
ST16 (n=51, 35,4%)
- Carbapenemase: KPC-2 (98,0%)
- ESBL: CTX-M-15 (78,4%)
- rmtB: 0%
- Mutações QRDR: 100% — GyrA-Ser83Phe + GyrA-Asp87Asn + ParC-Glu84Lys
- Porinas: OmpK35 (100%), OmpK36 (62,7%)
- Virulência: ybt+ (51,0%), clb+ (0%)
- mgrB: 15,7%
- Sorotipo: KL51 / O3γ
Conclusão: resistência extensa com KPC-2 + CTX-M-15, sem colibactina.
ST258 (n=26, 18,1%)
- Carbapenemase: KPC-2 (100%)
- ESBL: CTX-M-14 (100%) — associação exclusiva
- rmtB: 76,9%
- Mutações QRDR: 100% — GyrA-Ser83Ile + ParC-Ser80Ile
- Porinas: OmpK35 (100%), OmpK36 (96,2%)
- Virulência: ybt+ (88,5%), clb+ (34,6%)
- mgrB: 30,8%
- Sorotipo: KL107 / O2α.2
Conclusão: perfil mais resistente, com maior prevalência de rmtB (76,9%) e mutações em porinas.
Resistência a colistina
Distribuição geral
Dos 144 isolados, 125 tiveram CIM de colistina determinada por microdiluição em caldo (Sensititre™):
| Fenótipo | n | % |
|---|---|---|
| Resistente (CIM >2 mg/L) | 45 | 36,0% |
| Sensível (CIM ≤2 mg/L) | 80 | 64,0% |
Resistência por ST
| ST | Resistentes | Total testado | % Resistência |
|---|---|---|---|
| ST11 | 36 | 54 | 66,7% |
| ST16 | 7 | 46 | 15,2% |
| ST258 | 0 | 17 | 0% |
| ST147 | 1 | 2 | 50% |
| ST101 | 1 | 1 | 100% |
66,7% dos isolados ST11 testados são resistentes a colistina — a maior taxa entre todos os STs. Notavelmente, 82,2% dos resistentes (37/45) não possuem mutação detectável em mgrB, sugerindo mecanismos alternativos (PhoPQ, PmrAB, modificações de lipídio A, bombas de efluxo).
Mutações em mgrB identificadas
| Mutação | n | STs |
|---|---|---|
| mgrb:p.Lys2fs | 7 | ST16 |
| mgrb:p.Lys3fs | 5 | ST258 |
| mgrb:c.G69del | 3 | ST11 |
| mgrb:c.G116del | 3 | ST258 |
| mgrb:c.T68del | 1 | ST11 |
| mgrb:c.A133del | 1 | ST16 |
Nenhum gene mcr (mcr-1 a mcr-10) foi detectado na coleção.
Sorotipagem capsular
A sorotipagem por Kaptive revelou associações consistentes entre loci capsulares e STs:
| Locus K | ST principal | Locus O |
|---|---|---|
| KL64 | ST11 | O2α.1 |
| KL51 | ST16 | O3γ |
| KL107 | ST258 | O2α.2 |
Visão integrada
Conclusões dos resultados preliminares
- Dominância de KPC: 96,5% dos isolados são KPC-positivos, com emergência de NDM (2,8%) e um caso de co-produção
- Clones de alto risco: ST11, ST16 e ST258 representam 94,4% da coleção
- Resistência a fluoroquinolonas: praticamente universal (97,9%) por mutações QRDR
- Comprometimento de porinas: 75% com mutações em ambas OmpK35 e OmpK36
- Tolerância a desinfetantes: qacEΔ1 presente em 82,6% dos isolados — dado central para a hipótese deste doutorado