Caracterização genômica da resiliência ambiental de clones de alto risco de Klebsiella pneumoniae em UTIs brasileiras
Investigação do impacto seletivo de protocolos de desinfecção química
FAPESP — Doutorado BEPE — McMaster University BioProject PRJNA1185159
Visão geral
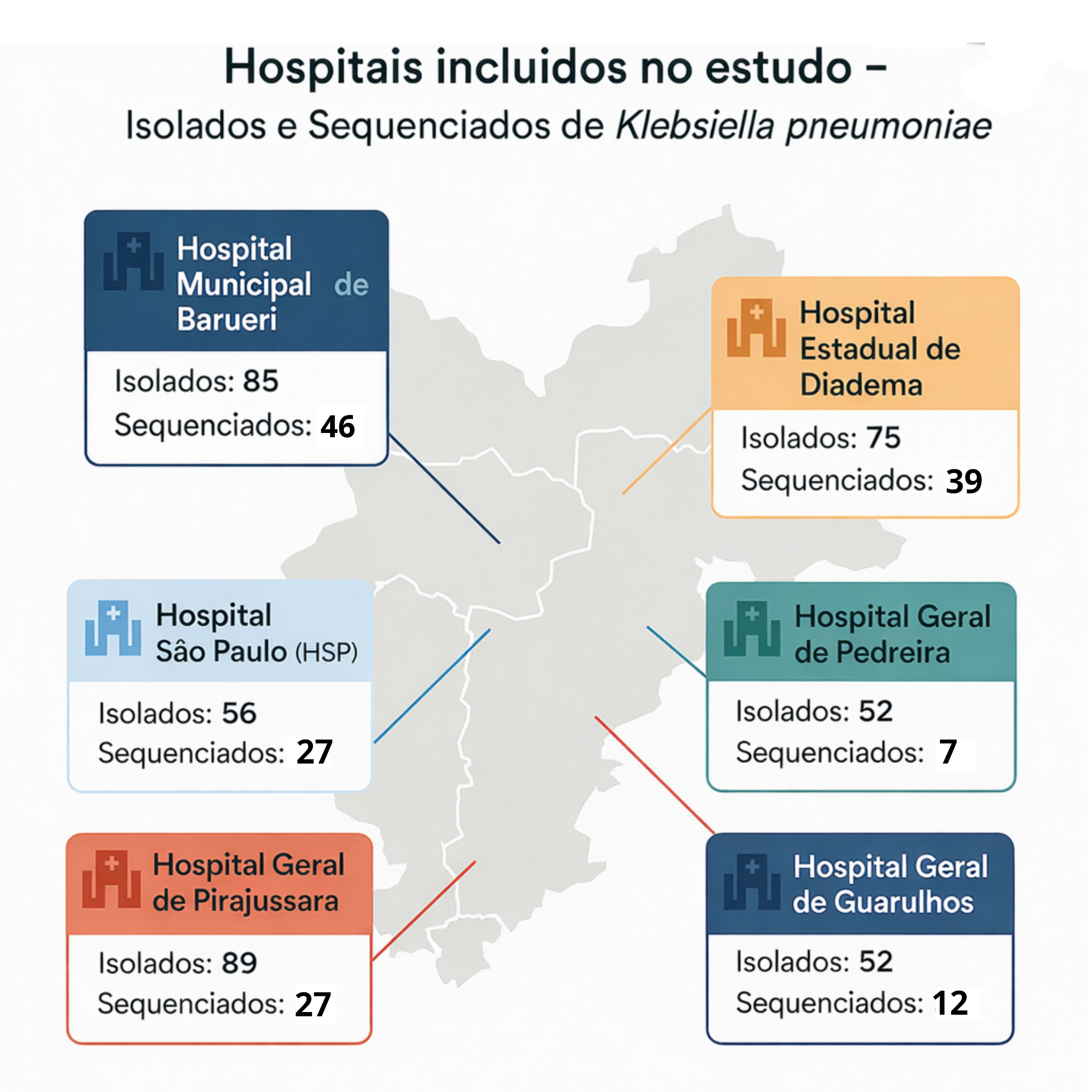
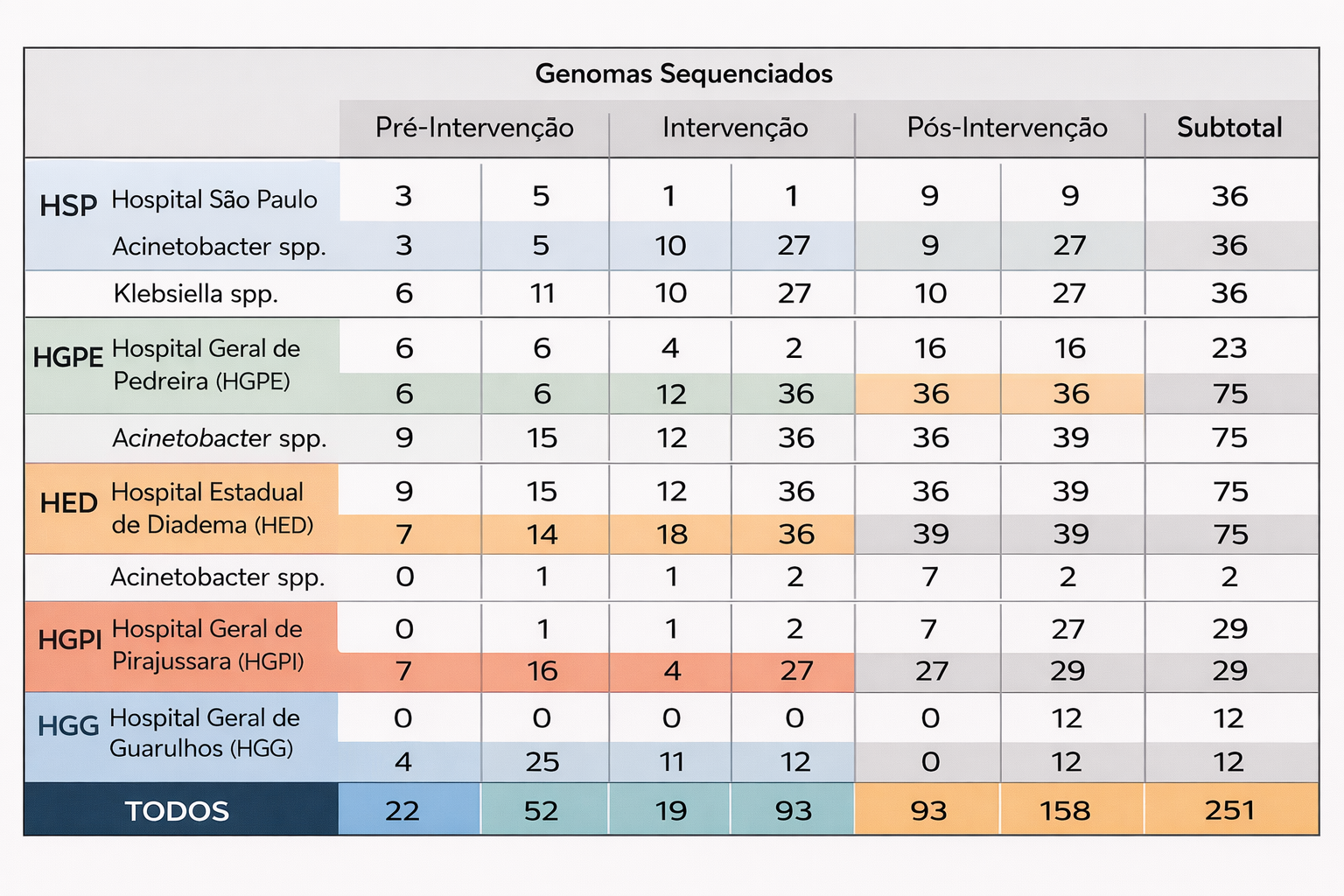
Este projeto de doutorado investiga os determinantes genômicos que permitem a clones de alto risco de Klebsiella pneumoniae resistente a carbapenêmicos persistir em superfícies de UTIs sob protocolos de desinfecção química de rotina. O trabalho parte de uma base multicêntrica já consolidada (Processo CNPq 408811/2022-6), integrando 144 genomas clínicos sequenciados com 27 isolados ambientais a serem sequenciados.
144 Genomas clínicos sequenciados
27 Isolados ambientais (a sequenciar)
6 UTIs — Grande São Paulo
406 Isolados totais recuperados
48 Meses de duração
12 Meses BEPE — Canadá
Contexto
A resistência antimicrobiana (RAM) é uma das principais ameaças à saúde pública global. K. pneumoniae resistente a carbapenêmicos é endêmica em UTIs brasileiras, com predomínio de clones de alto risco (ST11, ST16, ST258). Apesar da coleta ambiental sistemática durante o estudo precursor, os isolados ambientais ainda não foram sequenciados, impedindo a avaliação do vínculo epidemiológico em nível genômico.
Hipótese central
Protocolos de desinfecção química podem selecionar subpopulações de K. pneumoniae com determinantes de tolerância a biocidas (qac, smr, emr), sistemas de efluxo e genes de biofilme.
Abordagem
Filogenômica em nível de SNP, GWAS bacteriano, caracterização de resistoma/mobiloma e ensaios de tolerância a desinfetantes, integrando compartimentos clínico e ambiental.
Impacto esperado
Evidências para revisão de protocolos de desinfecção em hospitais do SUS e fortalecimento da vigilância genômica de patógenos de importância prioritária.
Mapa dos hospitais participantes
Visão integrada do estudo
Financiamento e afiliação
Programa de Pós-Graduação em Infectologia — Universidade Federal de São Paulo (UNIFESP)
- FAPESP — Bolsa de Doutorado + BEPE
- CNPq — Processo 408811/2022-6 (estudo multicêntrico precursor)
- CEPID ARIES — Processo FAPESP 2021/10599-3
